CSIRO Image2Biomass Prediction - 第5名Solo金牌方案,代码已开源!
更大的模型不一定更好:huge模型容易过拟合小数据集训练轮数需要控制:25轮左右是最佳平衡点复杂的注意力机制收益有限:在小数据集上容易过拟合Mamba等序列模型架构不适合此问题大量实验:做了188+次实验,充分探索了方案空间物理约束:利用目标之间的物理关系设计损失函数多样化融合:不同种子、不同架构、不同训练策略的模型融合数据增强:在小数据集上,合理的数据增强至关重要后处理:基于数据分析的后处理策略
首先感谢Kaggle和CSIRO组织这次比赛,这是一个非常有意义的农业AI应用场景。
1. 开场白
这是我第一次参加Kaggle CV比赛,很高兴也很幸运最后取得solo第五名(Private LB: 0.76)。在整个比赛过程中,我做了大量的实验——关于训练的实验我做了差不多100多次(从exp-v1到exp-v188)。通过这次比赛我学到了很多关于计算机视觉的知识,下面是关于我比赛方案的具体分享。
2. 比赛理解
2.1 问题描述
本次比赛的目标是使用牧场图像预测五个关键的生物质组分:
- Dry_Green_g - 干绿色植被(不包括三叶草)
- Dry_Dead_g - 干枯死物质
- Dry_Clover_g - 干三叶草生物质
- GDM_g - 绿色干物质
- Dry_Total_g - 总干生物质
2.2 数据特点
- 训练集规模较小:约800多张图像
- 图像尺寸:原始图像为2000x1000像素
- 存在分布差异:训练集和测试集分布有明显差异
- 多州数据:数据来自澳大利亚不同州(NSW, Tas, Vic, WA)
- 物理约束关系:目标之间存在物理关系
- Dead = Total - GDM
- Clover = GDM - Green
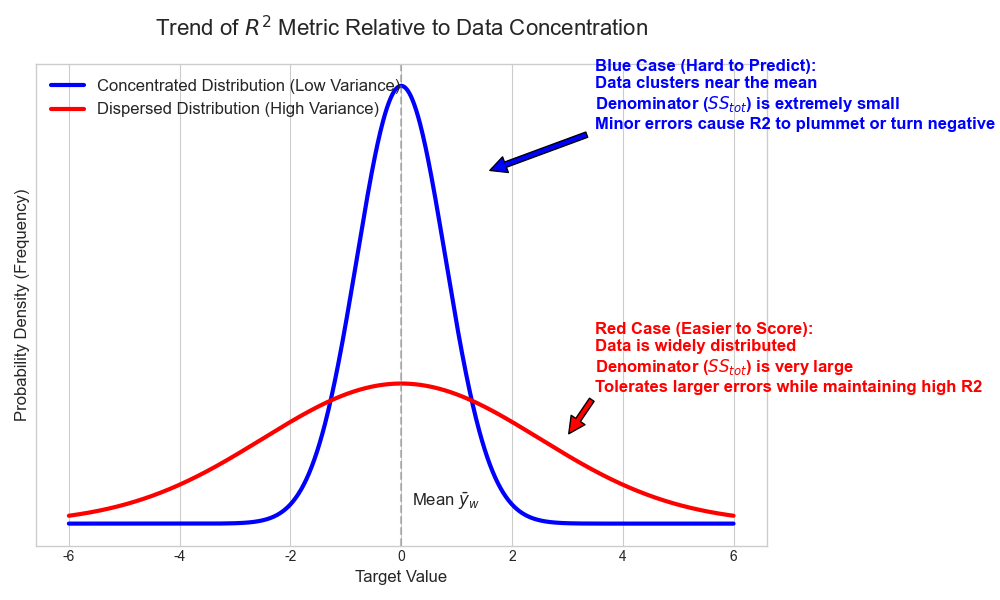
2.3 评估指标
比赛使用加权R²分数作为评估指标,对五个目标的R²进行加权平均。
3. 核心上分点
经过大量消融实验,以下是在当前方案上可以稳定上分的关键技术:
3.1 图像预处理 - 去除时间戳
原始图像中包含橙色的日期时间戳,这是一种数据噪声。我使用HSV颜色空间检测并使用图像修复技术去除这些时间戳:
def clean_image(img):
"""
图像预处理:去除底部伪影和日期戳
"""
# 在HSV空间检测橙色日期戳
hsv = cv2.cvtColor(img, cv2.COLOR_RGB2HSV)
# 定义橙色范围
lower = np.array([5, 150, 150])
upper = np.array([25, 255, 255])
mask = cv2.inRange(hsv, lower, upper)
# 膨胀掩码以覆盖文字边缘
mask = cv2.dilate(mask, np.ones((3, 3), np.uint8), iterations=2)
# 如果检测到时间戳,则进行修复
if np.sum(mask) > 0:
img = cv2.inpaint(img, mask, 3, cv2.INPAINT_TELEA)
return img

3.2 多种数据增强
由于训练集规模较小,数据增强对于防止过拟合至关重要。我使用了TTA风格的训练策略:
def get_tta_transforms(img_size: int) -> list[A.Compose]:
"""返回用于TTA风格训练的变换管道列表"""
normalize = A.Normalize(
mean=[0.485, 0.456, 0.406],
std=[0.229, 0.224, 0.225]
)
# View 0: 原始视图
original_view = A.Compose([
A.Resize(img_size, img_size),
normalize,
ToTensorV2()
])
# View 1: 水平翻转
hflip_view = A.Compose([
A.Resize(img_size, img_size),
A.HorizontalFlip(p=1.0),
normalize,
ToTensorV2()
])
# View 2: 垂直翻转
vflip_view = A.Compose([
A.Resize(img_size, img_size),
A.VerticalFlip(p=1.0),
normalize,
ToTensorV2()
])
# View 3: 旋转90度
rotate90_view = A.Compose([
A.Resize(img_size, img_size),
A.Rotate(limit=(90, 90), p=1.0, border_mode=0),
normalize,
ToTensorV2()
])
return [hflip_view, vflip_view, rotate90_view, original_view]
训练策略:
- 前15个epoch:使用增强视图(hflip, vflip, rotate90)进行训练,相当于4倍数据
- 后续epoch:仅使用原始视图
- 关键发现:随机选择增强方式比按epoch顺序选择效果更好(exp-v174)
3.3 多视图输入架构
除了将图像分为左右两半进行处理(模拟立体视觉),我还加入了完整图像作为第三个输入流:
class BiomassDataset(Dataset):
"""三流数据集:将2000x1000的图像分成左半、右半和完整图像"""
def __getitem__(self, idx: int):
image = self._load_image(self.image_paths[idx])
image = clean_image(image)
height, width = image.shape[:2]
mid = width // 2
left = image[:, :mid] # 左半部分
right = image[:, mid:] # 右半部分
full_image = image.copy() # 完整图像
# 对三个视图应用相同的变换
left = self.transform(image=left)["image"]
right = self.transform(image=right)["image"]
full_image = self.transform(image=full_image)["image"]
return left, right, full_image, train_tgt, eval_tgt, species_tgt
这种设计允许模型同时学习局部细节(左右视图)和全局上下文(完整视图)。
3.4 Mixture-of-Experts (MoE) 模型架构
设计初衷:模型能根据输入图像的具体情况(如是绿草多还是枯草多)自动切换最擅长的专家进行预测,从而有效解决多任务学习时的特征冲突。
class MetaMoE(nn.Module):
"""用于主要目标的混合专家头,输出均值和方差"""
def __init__(self, in_dim: int, hidden: int, num_experts: int,
out_dim: int = 1, dropout: float = 0.2):
super().__init__()
self.num_experts = num_experts
# 门控网络
self.gate = nn.Sequential(
nn.LayerNorm(in_dim),
nn.Linear(in_dim, 256),
nn.ReLU(),
nn.Linear(256, num_experts),
)
# 专家网络(每个输出均值和方差)
self.experts = nn.ModuleList([
nn.Sequential(
nn.LayerNorm(in_dim),
nn.Linear(in_dim, hidden),
nn.ReLU(),
nn.Dropout(dropout),
nn.Linear(hidden, 256),
nn.ReLU(),
nn.Linear(256, 2), # [mean, var_logit]
)
for _ in range(num_experts)
])
def forward(self, x: torch.Tensor):
gate_logits = self.gate(x)
gate_weights = F.softmax(gate_logits, dim=1).unsqueeze(-1)
expert_outs = torch.stack([expert(x) for expert in self.experts], dim=1)
out = (expert_outs * gate_weights).sum(dim=1)
pred_mean = out[:, 0:1]
pred_var_logit = out[:, 1:2]
pred_var = F.softplus(pred_var_logit) + 1e-6 # 确保方差为正
return pred_mean, pred_var
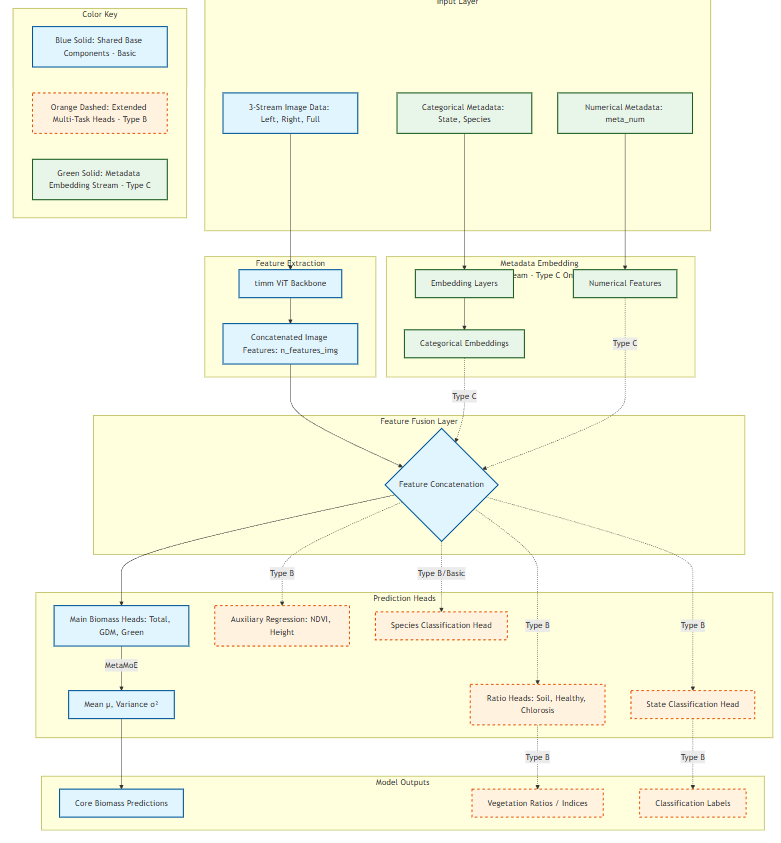
三种模型变体:
- Model Type A (BiomassModelBasic): 基础三流模型(exp-v147, exp-v164, exp-v174)
- Model Type B (BiomassModelWithStateSpecies): 带State/Species分类头(exp-v142)
- Model Type C (BiomassModelWithMetaEmbedding): 带元特征嵌入(exp-v148)
3.5 辅助训练头(Auxiliary Heads)
添加额外的训练目标可以帮助模型学习更丰富的特征表示:
class BiomassModel(nn.Module):
def __init__(self, model_name: str, pretrained: bool = True,
pretrained_path: str = '', num_species: int = 0):
super().__init__()
# ... backbone初始化 ...
# 主要回归头(使用MoE)
self.head_total = MetaMoE(...)
self.head_gdm = MetaMoE(...)
self.head_green = MetaMoE(...)
# 辅助回归头(NDVI和Height)
self.head_ndvi = _AuxHead(self.n_features, self.n_features // 2)
self.head_height = _AuxHead(self.n_features, self.n_features // 2)
# 可选的分类头
if num_species > 0:
self.head_species = self._make_classification_head(num_species)
辅助目标:
- Pre_GSHH_NDVI(归一化植被指数)
- Height_Ave_cm(平均牧草高度)
- Species(物种分类,15类)
- State(州分类,4类)
3.6 物理一致性损失(Physics Consistency Loss)
根据目标之间的物理关系设计损失函数,使用GaussianNLLLoss作为主要损失函数:
核心优势:
- 针对 R² 指标对离群点误差平方级敏感的特性
- 通过 GaussianNLL 自动降低高噪样本权重(避免被脏数据带偏)
- 利用物理约束锁定预测合理性(避免逻辑矛盾导致的巨大误差)
class PhysicsConsistencyLoss(nn.Module):
"""
物理一致性损失,使用GaussianNLLLoss
关键优势:
- 自动处理离群值:模型学习为噪声样本预测高方差
- 处理异方差性:不同生物质水平有不同的不确定性
- 物理约束:Dead = Total - GDM, Clover = GDM - Green
"""
def __init__(self, weights: dict[str, float] = None):
super().__init__()
self.w = {
"total": 0.45,
"gdm": 0.2,
"green": 0.1,
"dead": 0.1,
"clover": 0.1,
"ndvi": 0.0,
"height": 0.0,
"species": 0.05
}
self.criterion = nn.GaussianNLLLoss()
def forward(self, preds, targets, species_targets=None):
# 直接预测的损失
loss_total = self.criterion(pred_total_mean, gt_total, pred_total_var)
loss_gdm = self.criterion(pred_gdm_mean, gt_gdm, pred_gdm_var)
loss_green = self.criterion(pred_green_mean, gt_green, pred_green_var)
# 物理约束损失
# Dead = Total - GDM
pred_dead_mean = pred_total_mean - pred_gdm_mean
pred_dead_var = pred_total_var + pred_gdm_var
gt_dead = gt_total - gt_gdm
loss_dead = self.criterion(pred_dead_mean, gt_dead, pred_dead_var)
# Clover = GDM - Green
pred_clover_mean = pred_gdm_mean - pred_green_mean
pred_clover_var = pred_gdm_var + pred_green_var
gt_clover = gt_gdm - gt_green
loss_clover = self.criterion(pred_clover_mean, gt_clover, pred_clover_var)
# 加权总损失
total_loss = (
self.w["total"] * loss_total +
self.w["gdm"] * loss_gdm +
self.w["green"] * loss_green +
self.w["dead"] * loss_dead +
self.w["clover"] * loss_clover
)
return total_loss
3.7 分层学习率(Layer-wise Learning Rate)
为预训练的Backbone和新初始化的Head设置不同的学习率:
param_groups = []
for name, param in model.named_parameters():
if 'backbone' in name:
# Backbone使用较小学习率保留预训练能力
param_groups.append({
'params': param,
'lr': cfg.finetune_lr * cfg.backbone_lr_mult # 通常0.1
})
elif 'head' in name:
# Head使用较大学习率快速拟合
param_groups.append({
'params': param,
'lr': cfg.finetune_lr * cfg.head_lr_mult # 通常1.0
})
else:
param_groups.append({'params': param, 'lr': cfg.finetune_lr})
optimizer = optim.AdamW(param_groups, weight_decay=cfg.weight_decay)
原理:为预训练的Backbone设置较小学习率以保留其通用的特征提取能力(防止破坏预训练权重),同时为新初始化的Head设置较大学习率以快速拟合当前特定任务。
3.8 后处理策略
3.8.1 基于State的后处理
通过分析发现WA州的数据特点与其他州不同:
# WA州特殊处理:Dead为0,Total等于GDM
if predicted_states_df is not None:
final_pred = final_pred.merge(predicted_states_df, on='image_path', how='left')
is_wa = final_pred['Predicted_State'] == 'WA'
final_pred.loc[is_wa, 'Dry_Dead_g'] = 0
final_pred.loc[is_wa, 'Dry_Total_g'] = final_pred.loc[is_wa, 'GDM_g']
3.8.2 基于统计的范围截断
根据训练集各州的目标值统计范围进行结果截断:
state_stats = {
'Tas': {'Dry_Clover_g': {'min': 0.0, 'max': 71.79}, ...},
'NSW': {'Dry_Clover_g': {'min': 0.0, 'max': 10.10}, ...},
'WA': {'Dry_Clover_g': {'min': 0.0, 'max': 58.88}, ...},
'Vic': {'Dry_Clover_g': {'min': 0.0, 'max': 67.90}, ...}
}
for state in state_stats.keys():
state_mask = final_pred['Predicted_State'] == state
for var in target_vars:
min_val = state_stats[state][var]['min']
max_val = state_stats[state][var]['max']
final_pred.loc[state_mask, var] = final_pred.loc[state_mask, var].clip(
lower=min_val, upper=max_val
)
3.8.3 缩放后处理
def apply_post_processing(df: pd.DataFrame) -> pd.DataFrame:
"""应用Clover和Dead的后处理规则"""
df_out = df.copy()
if 'Dry_Clover_g' in df_out.columns:
df_out['Dry_Clover_g'] = df_out['Dry_Clover_g'] * 0.8
if 'Dry_Dead_g' in df_out.columns:
mask_high = df_out['Dry_Dead_g'] > 20
df_out.loc[mask_high, 'Dry_Dead_g'] *= 1.1
mask_low = df_out['Dry_Dead_g'] < 10
df_out.loc[mask_low, 'Dry_Dead_g'] *= 0.9
return df_out
3.9 全量数据集训练
因为训练集比较小,初衷是利用上所有数据集,仅仅过拟合训练集。
# train_df = df[df["fold"] != fold].reset_index(drop=True)
# valid_df = df[df["fold"] == fold].reset_index(drop=True)
train_df = df
valid_df = df
4. 模型融合
4.1 最终融合方案
最终提交使用了6个模型的加权融合:
| 模型 | 权重 | 特点 |
|---|---|---|
| exp-v142 | 0.0 (仅用于State预测) | BiomassModelWithStateSpecies,提取State信息 |
| exp-v148 | 0.15 | BiomassModelWithMetaEmbedding,利用元特征 |
| exp-v147 | 0.20 | BiomassModelBasic,seed=2026 |
| exp-v174 | 0.25 | BiomassModelBasic,随机数据增强 |
| exp-v164 | 0.20 | BiomassModelBasic,TTA式数据增强 |
| exp-v177 | 0.20 | BiomassModelBasic,调整损失权重 |
4.2 TTA推理
每个模型使用3种TTA变换:
- 原始视图
- 水平翻转
- 垂直翻转
最终预测取平均值。
4.3 双GPU并行推理
为了加速推理,实现了双GPU并行推理:
def parallel_dual_gpu_inference(dataset, model_class, model_kwargs, model_states, ...):
"""在两个GPU上并行运行推理"""
# 偶数索引 -> GPU 0,奇数索引 -> GPU 1
indices_0 = list(range(0, n, 2))
indices_1 = list(range(1, n, 2))
with ThreadPoolExecutor(max_workers=2) as executor:
future_0 = executor.submit(inference_single_gpu, model_0, ..., device_0)
future_1 = executor.submit(inference_single_gpu, model_1, ..., device_1)
results_0 = future_0.result()
results_1 = future_1.result()
# 合并结果
...
5. 关键超参数
| 超参数 | 值 |
|---|---|
| Backbone | vit_large_patch16_dinov3_qkvb |
| 图像尺寸 | 1024x1024 |
| Batch Size | 4 |
| 学习率 | 2e-4 (warm-up后finetune为5e-5) |
| Backbone学习率倍率 | 0.1 |
| 训练轮数 | 25 |
| MoE专家数 | 4 |
| MoE隐藏层维度 | 512 |
| 优化器 | AdamW |
| Weight Decay | 1e-4 |
6. 失败的尝试
根据实验记录,以下方法没有带来提升或效果不稳定:
6.1 没有效果的方法
| 实验 | 描述 | 结果 |
|---|---|---|
| exp-v36 | 使用比率预测 | CV从0.58降到0.43 |
| exp-v97 | 整张图片不分流 | CV 0.57, LB 0.52(严重下降) |
| exp-v99 | 学习率2e-4+20轮 | CV仅0.21 |
| exp-v123 | 分割图像+注意力 | CV 0.53, LB 0.53 |
| exp-v168/169 | Mamba Network | CV 0.80-0.89(不稳定) |
| exp-v180 | UNet原尺寸1000x2000 | LB 0.64(下降明显) |
6.2 效果不稳定的方法
| 实验 | 描述 | 问题 |
|---|---|---|
| Huge模型 (exp-v170) | vit_huge | CV很高0.95但LB 0.72 |
| 30轮训练 (exp-v161) | 增加训练轮数 | 过拟合,Private LB下降 |
| 多种分割mask | ng/xg mask | 部分有效但不稳定 |
6.3 经验总结
- 更大的模型不一定更好:huge模型容易过拟合小数据集
- 训练轮数需要控制:25轮左右是最佳平衡点
- 复杂的注意力机制收益有限:在小数据集上容易过拟合
- Mamba等序列模型架构不适合此问题
7. 实验进展历程
7.1 分数提升关键节点
| 阶段 | 实验 | Public LB | Private LB | 关键改进 |
|---|---|---|---|---|
| 基线 | v1 | 0.57 | - | 448尺寸baseline |
| 模型升级 | v24 | 0.65 | - | vit_large_dinov3 |
| 分辨率 | v32 | 0.69 | - | 512尺寸 |
| 物理Loss | v42 | 0.69+ | - | PhysicsConsistencyLoss |
| MoE | v44 | 0.69 | - | 混合专家架构 |
| 1024分辨率 | v108 | 0.73 | - | 1024尺寸+学习率优化 |
| 全量训练 | v136 | 0.74+ | - | 全量数据集+Species |
| 种子优化 | v147 | 0.75+ | - | seed=2026 |
| 数据增强 | v164 | 0.75 | - | TTA式数据增强 |
| 随机增强 | v174 | 0.76 | 0.65 | 随机选择增强方式 |
| 融合 | 最终 | 0.76 | 0.66 | 6模型加权融合 |
7.2 最终Private LB分数分布
根据提交记录,选中的两个最终提交:
- Public LB: 0.76, Private LB: 0.66(第5名)
8. 总结与经验分享
8.1 成功的关键因素
- 大量实验:做了188+次实验,充分探索了方案空间
- 物理约束:利用目标之间的物理关系设计损失函数
- 多样化融合:不同种子、不同架构、不同训练策略的模型融合
- 数据增强:在小数据集上,合理的数据增强至关重要
- 后处理:基于数据分析的后处理策略
8.2 关于选分
这次比赛选分非常困难,主要原因:
- 数据集规模小,模型容易过拟合
- 训练集和测试集分布存在差异
- Public LB和Private LB相关性不高
我最终选择了Public LB最高的提交,虽然Private LB不是最优(0.66 vs 某些失败提交的0.65),但相对稳定。
8.3 运气成分
必须承认这次成绩有一定的运气成分:
- 看到前排很多大佬在shake-up中抖动
- 选分策略恰好没有踩坑
- 多模型融合提高了稳定性
8.4 致谢
非常感谢:
- Kaggle社区的无私分享
- 各位Kaggler的讨论和notebook
- CSIRO组织方提供这个有意义的比赛
这次solo金牌对于我成为Grandmaster非常重要!希望这份方案分享能帮助到大家。
代码仓库:完整的训练和推理代码请参考比赛提交的notebook。
最终提交Notebook: CSIRO-Ensemble-Models-V12
更多推荐
 已为社区贡献19条内容
已为社区贡献19条内容






所有评论(0)