DL00600:基于U-Net模型实现脑部MRI定位源码
注意,这里的输入大小是256x256的单通道图像(灰度图),输出是同样大小的单通道图像,表示分割结果。编码器部分负责提取图像的特征,而解码器部分则负责将提取的特征还原为分割结果。通过合理的预处理和模型训练,我们可以得到不错的分割结果。当然,实际应用中可能还需要考虑更多的细节,比如数据增强、模型调参等。Unet模型在图像分割领域可是个老熟人了,尤其是在医学图像处理上,表现相当出色。我们先来看看Une
DL00600-基于Unet模型实现脑部MRI定位源码
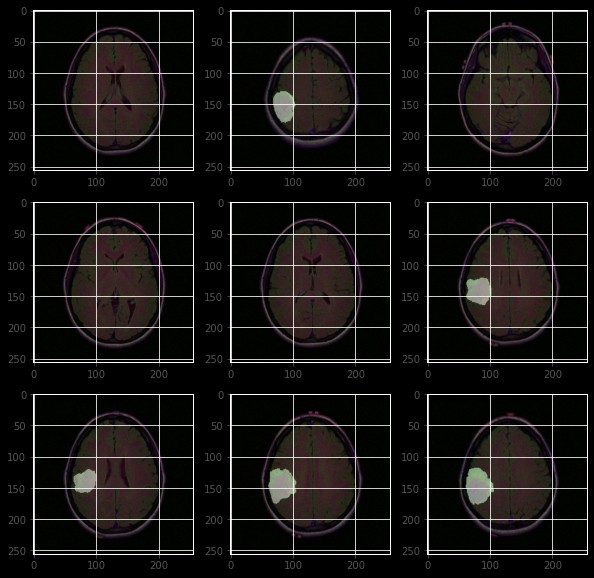
今天我们来聊聊如何用Unet模型实现脑部MRI的定位。Unet模型在图像分割领域可是个老熟人了,尤其是在医学图像处理上,表现相当出色。我们先来看看Unet的基本结构,然后再通过代码一步步实现脑部MRI的定位。
DL00600-基于Unet模型实现脑部MRI定位源码
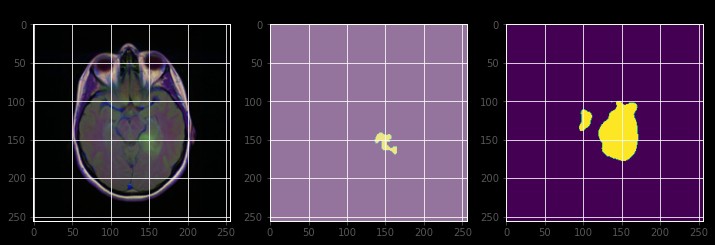
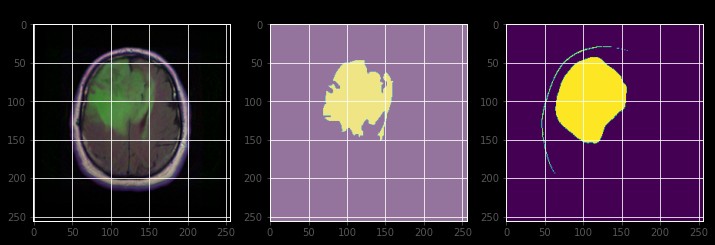
Unet的结构可以简单理解为“编码器-解码器”架构。编码器部分负责提取图像的特征,而解码器部分则负责将提取的特征还原为分割结果。中间的跳跃连接(skip connections)则是Unet的“灵魂”,它帮助模型更好地保留细节信息。
import tensorflow as tf
from tensorflow.keras.layers import Input, Conv2D, MaxPooling2D, Dropout, UpSampling2D, concatenate
def unet(input_size=(256, 256, 1)):
inputs = Input(input_size)
conv1 = Conv2D(64, 3, activation='relu', padding='same')(inputs)
conv1 = Conv2D(64, 3, activation='relu', padding='same')(conv1)
pool1 = MaxPooling2D(pool_size=(2, 2))(conv1)
conv2 = Conv2D(128, 3, activation='relu', padding='same')(pool1)
conv2 = Conv2D(128, 3, activation='relu', padding='same')(conv2)
pool2 = MaxPooling2D(pool_size=(2, 2))(conv2)
# 中间部分
conv3 = Conv2D(256, 3, activation='relu', padding='same')(pool2)
conv3 = Conv2D(256, 3, activation='relu', padding='same')(conv3)
pool3 = MaxPooling2D(pool_size=(2, 2))(conv3)
# 解码器部分
up4 = UpSampling2D(size=(2, 2))(conv3)
up4 = concatenate([up4, conv2], axis=3)
conv4 = Conv2D(128, 3, activation='relu', padding='same')(up4)
conv4 = Conv2D(128, 3, activation='relu', padding='same')(conv4)
up5 = UpSampling2D(size=(2, 2))(conv4)
up5 = concatenate([up5, conv1], axis=3)
conv5 = Conv2D(64, 3, activation='relu', padding='same')(up5)
conv5 = Conv2D(64, 3, activation='relu', padding='same')(conv5)
# 输出层
outputs = Conv2D(1, 1, activation='sigmoid')(conv5)
model = tf.keras.Model(inputs=inputs, outputs=outputs)
return model这段代码定义了一个简单的Unet模型。编码器部分通过卷积和池化操作逐步提取特征,解码器部分则通过上采样和跳跃连接将特征还原为分割结果。注意,这里的输入大小是256x256的单通道图像(灰度图),输出是同样大小的单通道图像,表示分割结果。
接下来,我们需要准备数据。脑部MRI数据通常以NIfTI格式存储,我们可以使用nibabel库来读取这些数据。
import nibabel as nib
def load_nifti(file_path):
img = nib.load(file_path)
data = img.get_fdata()
return data加载数据后,我们还需要对数据进行预处理。MRI图像的像素值范围通常较大,我们需要将其归一化到[0, 1]之间。
import numpy as np
def normalize_image(image):
image = image.astype(np.float32)
image = (image - np.min(image)) / (np.max(image) - np.min(image))
return image有了数据和模型,我们就可以开始训练了。这里我们使用二元交叉熵作为损失函数,Adam优化器。
model = unet()
model.compile(optimizer='adam', loss='binary_crossentropy', metrics=['accuracy'])
# 假设我们已经准备好了训练数据和标签
# X_train, y_train = ...
model.fit(X_train, y_train, batch_size=16, epochs=20, validation_split=0.2)训练完成后,我们可以用模型对新的MRI图像进行预测。
def predict_image(model, image):
image = np.expand_dims(image, axis=0)
prediction = model.predict(image)
return prediction[0]最后,别忘了保存模型,以便后续使用。
model.save('brain_mri_unet.h5')总的来说,使用Unet模型进行脑部MRI定位并不复杂。通过合理的预处理和模型训练,我们可以得到不错的分割结果。当然,实际应用中可能还需要考虑更多的细节,比如数据增强、模型调参等。希望这篇文章能给你带来一些启发,快去试试吧!
更多推荐
 已为社区贡献13条内容
已为社区贡献13条内容






所有评论(0)